丙氨酸十二肽的折叠
SPONGE 1.4 教程。丙氨酸十二肽的折叠
更新时间:
2024/01/01
主要内容:
- 使用Xponge构建一个丙氨酸十二肽的隐式溶剂模型
- 使用SPONGE的1.4版本模拟
- 使用VMD可视化
软件安装
建模
打开终端,呼出python
python
在python终端内,依次输入下面的python命令
1. 导入需要的模块
import Xponge #Xponge本体
import Xponge.forcefield.amber.ff19sb #使用的力场
from Xponge.forcefield.special import gb #使用的隐式溶剂模型GB
2. 获得Xponge的分子实例
mol = NALA + ALA * 10 + CALA
3. 设置GB参数
gb.Set_GB_Radius(mol)
4. 保存输入文件
Save_PDB(mol, "ALA.pdb")
Save_SPONGE_Input(mol, "ALA")
动力学模拟
在文件夹里用你喜欢的文本编辑器构建mdin.txt文件:
ALA12 simulation
pbc = 0
mode = NVT
dt = 2e-3
cutoff = 999
constrain_mode = SHAKE
step_limit = 5000000
thermostat = middle_langevin
default_in_file_prefix = ALA
各命令的含义可见输入命令
然后在终端里输入命令
SPONGE -mdin mdin.txt
分析与讨论
结果分析
可读取生成的mdout.txt获取能量数据。使用下面的python脚本读取能量变化数据
from Xponge.analysis import MdoutReader
mdout = MdoutReader("mdout.txt")
import matplotlib.pyplot as plt
plt.plot(mdout.time, mdout.potential)
plt.show()
可得
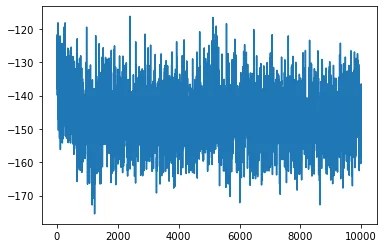
也可以使用VMD对轨迹可视化
vmd -sponge_mass ./ALA_mass.txt mdcrd.dat

